Identificación de proteínas en Candidatus Liberibacter asiaticus para desarrollar un método de detección inmunoenzimático
DOI:
https://doi.org/10.29312/remexca.v13i8.3355Palabras clave:
diagnóstico, huanglongbing, serologíaResumen
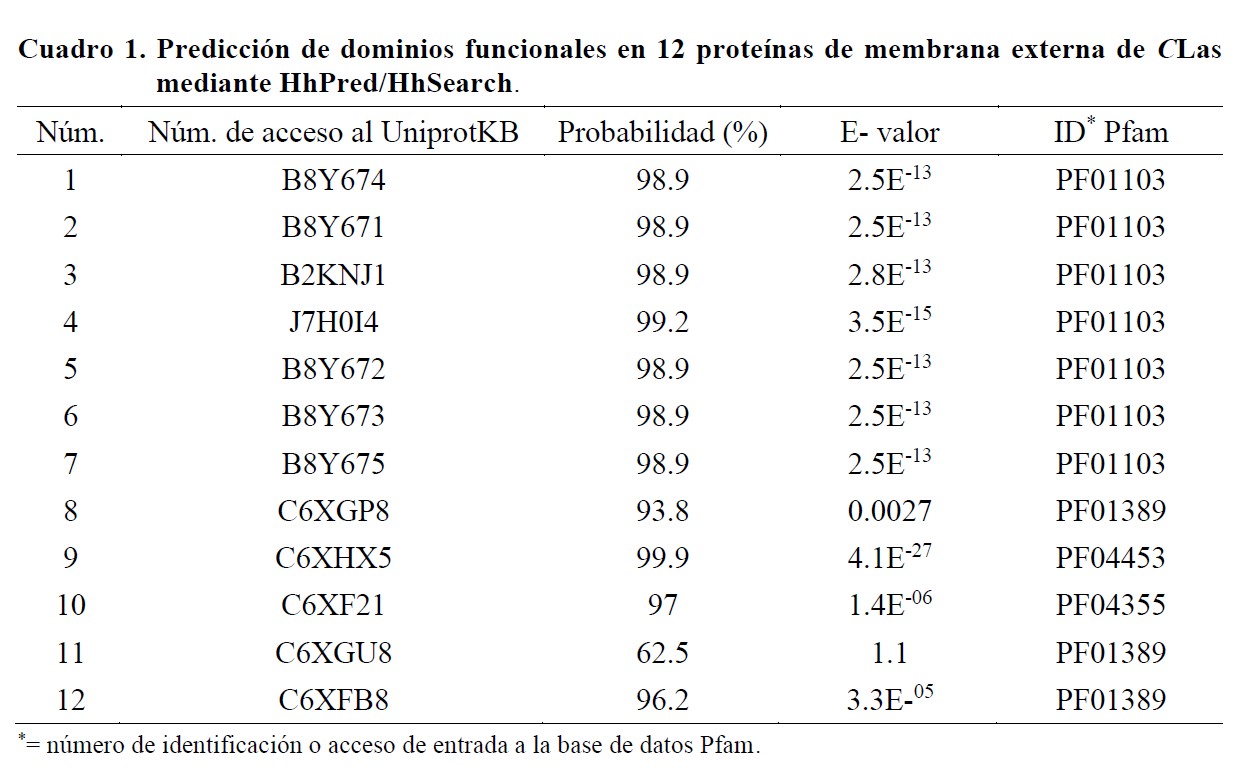
El objetivo de este trabajo fue identificar en el genoma de Candidatus Liberibacter asiaticus (CLas), proteínas de membrana externa con potencial para el desarrollo y optimización de un método de detección inmunoenzimático. El estudio se realizó durante 2019 y se utilizó el servidor web Predict Protein, así como las bases de datos HhPred/HhSearch y Pfam. Se detectaron 52 proteínas de membrana externa en el genoma completo de CLas, de las cuales, 11 no habían sido caracterizadas previamente. Los análisis predictivos realizados en la proteína B8Y674 generaron ocho posibles epítopos y cuatro de ellos evaluados experimentalmente en células B, mostraron porcentajes de identidad entre 80 a 90%. Se detectó a CLas mediante PCR-punto final a partir del ADN extraído de limón mexicano con síntomas de Huanglongbing utilizando iniciadores diseñados sobre la secuencia del gen Omp que codifica para la proteína B8Y674 y se registró 95% de identidad entre las secuencias generadas y secuencias de CLas previamente reportadas. Los resultados obtenidos nos permiten inferir que la proteína B8Y674 es un candidato potencial para ser utilizada en la detección inmunoenzimática de CLas.
Descargas
Referencias
Achor, D. S.; Welker, S.; Ben-Mahmoud, S.; Wang, C.; Folimonova. S. Y.; Dutt, M.; Gowda, S. and Levy, A. 2020. Dynamics of Candidatus Liberibacter asiaticus movement and sieve pore plugging in citrus sink cells. Plant Physiol. 182(2):882-891. Doi: 10.1104/pp.19.01391.
Andrade, M. O.; Pang, Z.; Achor, D. S.; Wang, H.; Yao, T.; Singer, B. H. and Wang, N. 2020. The flagella of “Candidatus Liberibacter asiaticus” and its movement in planta. Molecular plant pathology. 21(1):109-123. Doi: 10.1111/mpp.12884.
Bastianel, C.; Garnier-Semancik, M.; Renaudin, J.; Bové, J. M. and Eveillard, S. 2005. Diversity of “Candidatus Liberibacter asiaticus,” based on the omp gene sequence. Appl. Environ. Microbiol. 71(11):6473-6478. Doi: 10.1128/AEM.71.11.6473-6478.2005.
Carrizo, A.; Brihuega, B.; Etchechoury, I.; Arese, A.; Romero, S.; Gioffré, A., Romano, M. F. and Caimi, K. 2009. Identification of immunoreactive antigens of Leptospira interrogans. Rev. Argentina de Microbiol. 41(3):129-133.
Chen, J.; Deng, X.; Sun, X.; Jones, D.; Irey, M. and Civerolo, E. 2010. Guangdong and Florida populations of ‘Candidatus Liberibacter asiaticus’ distinguished by a genomic locus with short tandem repeats. Phytopathology. 100(6):567-572. Doi: 10.1094/PHYTO-100-6-0567.
Conesa, A.; Gotz, S.; García-Gómez. J. M.; Terol, J.; Talón, M. and Robles, M. 2005. Blast2GO: a universal tool for annotation, visualization and analysis in functional genomics research. Bioinformatics. 21(18):3674-3676.
Ding, F.; Duan, Y.; Paul, C.; Brlansky, R. H. and Hartung, J. S. 2015. Localization and Distribution of “Candidatus Liberibacter asiaticus” in citrus and periwinkle by direct tissue blot immuno assay with an anti ompa polyclonal antibody. Plos One. 10(5):e0123939-10. http://doi.org/ 10.1371/journal.pone.0123939.
Fundora, H. H.; Puig, P. Y.; Chiroles, R. S.; Rodríguez, B. A. M.; Gallardo, D. J. y Milián, S. Y. 2013. Métodos inmunológicos utilizados en la identificación rápida de bacterias y protozoarios en aguas. Rev. Cubana de Hig. Epidemiol. 51(1):84-96.
Lin, H.; Han, C. S.; Liu, B.; Lou, B.; Bai, X.; Deng, C.; Civerolo, E. L. and Gupta, G. 2013. Complete genome sequence of a chinese strain of “Candidatus Liberibacter asiaticus”. Genome Announcements. 1(2):e00184-13. Doi: 10.1128/genomeA.00184-13.
Lu, L.; Cheng, B.; Yao, J.; Peng, A.; Du, D.; Fan, G.; Hu, X.; Zhang, L. and Chen, G. 2013. A new diagnostic system for detection of ‘Candidatus Liberibacter asiaticus’ infection in citrus. Plant Dis. 97(10):1295-1300. http://dx.doi.org/10.1094/ PDIS-11-12-1086-RE.
Mauri, C. and Bosma, A. 2012. Immune regulatory function of b cells. Annual Review of Immunol. 30:221-242. Doi: 10.1146/annurev-immunol-020711-074934.
McCollum, G.; Hilf, M.; Irey, M.; Luo, W. and Gottwald, T. 2016. Susceptibility of sixteen citrus genotypes to ‘Candidatus Liberibacter asiaticus’. Plant Dis. 100(6):1080-1086. http://dx.doi.org/10.1094/PDIS-08-15-0940-RE.
Rodríguez, Q. C. G.; Alanís, M. E. I.; Velázquez, M. J. J. y Almeyda, L. I. H. 2010. Optimización de la técnica de extracción del DNA de plantas de cítricos para el diagnóstico del HLB. En 1er. simposio nacional sobre investigación para el manejo del psílido asiático de los cítricos y el huanglongbing en México. Monterrey, Nuevo León. 22-29 pp.
Rodríguez, Q. C. G.; Almeyda, L. I. H.; Alvarez, O. M. G.; Hernández, G. C. y Mendoza, H. A. 2018. Detección de Candidatus liberibacter asiaticus mediante PCR-punto final, utilizando iniciadores diseñados a partir de los genes omp y clibasia-02425. In: memoria del XXX1 Simposio de avances en Investigación Agrícola, Pecuaria, Forestal, Acuícola, Pesquería, Desarrollo Rural, Transferencia de Tecnología, Biotecnología, Ambiente, Recursos Naturales y Cambio Climático. Veracruz. 1644-1655 pp.
Söding, J.; Biegert, A. and Lupas, A. N. 2005. The HHpred interactive server for protein homology detection and structure prediction. Nucleic Acids Res. 33(2):244-248. Doi: 10.1093/nar/ gki408.
Tomimura, K.; Miyata, S.; Furuya, N.; Kubota, K.; Okuda, M.; Subandiyah, S.; Hung, T.; Su, H. J. and Iwanami, T. 2009. Evaluation of genetic diversity among ‘Candidatus Liberibacter asiaticus’ isolates collected in southeast Asia. Phytopathology. 99(9):1062-1069. Doi: 10.1094/PHYTO-99-9-1062.
Yuan, Q.; Jordan, R.; Brlansky, R. H.; Minenkova, O. and Hartung, J. 2016. Development of single chain variable fragment (scFv) antibodies against surface proteins of ‘Ca. Liberibacter asiaticus’. J. Microbiol. Methods. 122:1-7. Doi: 10.1016/j.mimet.2015.12.015.
Zherdev, A. V.; Vinogradova, S. V.; Byzova, N. A.; Porotikova, E. V.; Kamionskaya, A. M. and Dzantiev, B. B. 2018. Methods for the diagnosis of grapevine viral infections: a review. Agriculture. 8(12):1-19. Doi: 10.3390/agriculture8120195.
Descargas
Publicado
Número
Sección
Licencia
Derechos de autor 2022 Revista Mexicana de Ciencias Agrícolas

Esta obra está bajo una licencia internacional Creative Commons Atribución-NoComercial 4.0.
Los autores(as) que publiquen en Revista Mexicana de Ciencias Agrícolas aceptan las siguientes condiciones:
De acuerdo con la legislación de derechos de autor, Revista Mexicana de Ciencias Agrícolas reconoce y respeta el derecho moral de los autores(as), así como la titularidad del derecho patrimonial, el cual será cedido a la revista para su difusión en acceso abierto.
Los autores(as) deben de pagar una cuota por recepción de artículos antes de pasar por dictamen editorial. En caso de que la colaboración sea aceptada, el autor debe de parar la traducción de su texto al inglés.
Todos los textos publicados por Revista Mexicana de Ciencias Agrícolas -sin excepción- se distribuyen amparados bajo la licencia Creative Commons 4.0 atribución-no comercial (CC BY-NC 4.0 internacional), que permite a terceros utilizar lo publicado siempre que mencionen la autoría del trabajo y a la primera publicación en esta revista.
Los autores/as pueden realizar otros acuerdos contractuales independientes y adicionales para la distribución no exclusiva de la versión del artículo publicado en Revista Mexicana de Ciencias Agrícolas (por ejemplo incluirlo en un repositorio institucional o darlo a conocer en otros medios en papel o electrónicos) siempre que indique clara y explícitamente que el trabajo se publicó por primera vez en Revista Mexicana de Ciencias Agrícolas.
Para todo lo anterior, los autores(as) deben remitir el formato de carta-cesión de la propiedad de los derechos de la primera publicación debidamente requisitado y firmado por los autores(as). Este formato debe ser remitido en archivo PDF al correo: revista_atm@yahoo.com.mx; revistaagricola@inifap.gob.mx.
Esta obra está bajo una licencia de Creative Commons Reconocimiento-No Comercial 4.0 Internacional.


